Courbes PES de dissociation avec Qunova HiVQE
Les fonctions Qiskit sont une fonctionnalité expérimentale disponible uniquement pour les utilisateurs des plans IBM Quantum® Premium, Flex et On-Prem (via l'API IBM Quantum Platform). Elles sont en version préliminaire et susceptibles d'être modifiées.
Estimation d'utilisation (REMARQUE : Ceci est uniquement une estimation. Votre temps d'exécution peut varier.)
- Li2S : cinq minutes de temps QPU sur un processeur Heron r2
- FeP-NO : cinq minutes de temps QPU sur un processeur Heron r2
Contexte
Le calcul précis des énergies de réaction chimique est essentiel pour les avancées scientifiques en science des matériaux, en génie chimique, en découverte de médicaments et dans d'autres domaines. Parmi les différents systèmes chimiques, le système Li-S a suscité un intérêt significatif pour la compréhension et le développement de nouvelles compositions de batteries. Ce tutoriel t'offre une expérience pratique du calcul de la surface d'énergie potentielle (PES) de dissociation de la liaison Li-S d'un système en retirant un atome de lithium à l'aide de calculs HiVQE. Les résultats peuvent être comparés avec des calculs de référence (CASCI) ainsi qu'avec des méthodes classiques comme Hartree-Fock (HF) pour un problème à 20 qubits.
Prérequis
Installez les dépendances suivantes pour exécuter le code de ce tutoriel.
!pip install --upgrade pip
!pip install -U qiskit-ibm-catalog "qiskit_ibm_runtime<0.42.0" pyscf numpy matplotlib typing_extensions
Configuration
Pour exécuter ce tutoriel, importez la fonction qunova/hivqe-chemistry via QiskitFunctionCatalog. Vous avez besoin d'un compte IBM Quantum avec un plan Premium, Flex ou On-Prem (API IBM Quantum Platform) et d'une licence Qunova pour exécuter cette fonction.
from qiskit_ibm_catalog import QiskitFunctionsCatalog
from pyscf import gto, scf, mcscf
import matplotlib.pyplot as plt
import pprint
catalog = QiskitFunctionsCatalog(
channel="ibm_quantum_platform",
instance="INSTANCE_CRN",
token="YOUR_API_KEY", # Use the 44-character API_KEY you created and saved from the IBM Quantum Platform Home dashboard
)
hivqe = catalog.load("qunova/hivqe-chemistry")
Partie 1 : Li2S (20Q)
Étape 1 : Mapper les entrées classiques sur un problème quantique
Définissez les géométries de au format dictionnaire pour différentes distances de liaison Li-S afin de calculer la courbe PES. Ces géométries sont optimisées à l'aide de calculs B3LYP/631g.
str_geometries = {
"1.51": "S -1.239044 0.671232 -0.030374; Li -1.506327 0.432403 -1.498949; Li -0.899996 0.973348 1.826768",
"1.91": "S -1.215858 0.692272 0.099232; Li -1.553305 0.390283 -1.758043; Li -0.876205 0.994426 1.956257",
"2.40": "S -1.741432 0.680397 0.346702; Li -0.529307 0.488006 -1.729343; Li -1.284307 0.989409 2.177209",
"3.10": "S -2.347450 0.657089 0.566194; Li -0.199353 0.527517 -1.665148; Li -1.008243 0.973206 1.893522",
"3.80": "S -2.707255 0.674298 0.909161; Li 0.079218 0.552012 -1.671656; Li -0.927010 0.931502 1.557063",
"4.50": "S -2.913363 0.709175 1.276987; Li 0.368656 0.559989 -1.798088; Li -1.010340 0.888647 1.315670",
}
str_geometries
{'1.51': 'S -1.239044 0.671232 -0.030374; Li -1.506327 0.432403 -1.498949; Li -0.899996 0.973348 1.826768',
'1.91': 'S -1.215858 0.692272 0.099232; Li -1.553305 0.390283 -1.758043; Li -0.876205 0.994426 1.956257',
'2.40': 'S -1.741432 0.680397 0.346702; Li -0.529307 0.488006 -1.729343; Li -1.284307 0.989409 2.177209',
'3.10': 'S -2.347450 0.657089 0.566194; Li -0.199353 0.527517 -1.665148; Li -1.008243 0.973206 1.893522',
'3.80': 'S -2.707255 0.674298 0.909161; Li 0.079218 0.552012 -1.671656; Li -0.927010 0.931502 1.557063',
'4.50': 'S -2.913363 0.709175 1.276987; Li 0.368656 0.559989 -1.798088; Li -1.010340 0.888647 1.315670'}
Les calculs HiVQE seront effectués avec les options définies ci-dessous. En utilisant la base sto3g pour , il y a 19 orbitales spatiales avec 22 électrons. Pour exécuter le cas (10o,10e) avec un calcul HiVQE, tu peux définir 10 orbitales actives et six orbitales gelées. À chaque itération, 100 shots seront utilisés pour échantillonner la configuration électronique générée par le circuit quantique ExcitationPreserving (epa) avec un enchevêtrement circular et deux répétitions (reps). Le nombre maximum d'itérations est fixé à 30 pour garantir la terminaison de l'itération avec convergence de l'énergie.
molecule_options = {
"basis": "sto3g",
"active_orbitals": list(range(5, 15)),
"frozen_orbitals": list(range(5)),
}
hivqe_options = {
"shots": 100,
"max_iter": 30,
"ansatz": "epa",
"ansatz_entanglement": "circular",
"ansatz_reps": 2,
}
Étapes 2 et 3 : Optimiser le problème pour l'exécution sur matériel quantique et exécuter avec la fonction HiVQE Chemistry
Configurez la boucle for pour exécuter les calculs HiVQE avec les géométries et les options définies ci-dessous. Les tâches sont soumises dans la boucle for. Dans ce tutoriel, tu soumettras six géométries et récupéreras les résultats lorsqu'elles seront toutes terminées. Dans l'exécution de la fonction principale, tu dois définir max_states et max_expansion_states pour contrôler la taille maximale de la matrice de sous-espace et le nombre d'états pouvant être générés à l'aide de méthodes d'expansion CI classiques par itération. Les identifiants de tâches de la fonction seront stockés dans le dictionnaire avec chaque étiquette de géométrie pour suivre et traiter les résultats ultérieurement.
info_jobid = {}
for dis, geom in str_geometries.items():
hivqe_run = hivqe.run(
geometry=geom,
backend_name="",
max_states=40000,
max_expansion_states=100,
molecule_options=molecule_options,
hivqe_options=hivqe_options,
)
status = hivqe_run.status()
info_jobid[dis] = hivqe_run.job_id
print(info_jobid)
{'1.51': 'de3b8818-c9db-4fa3-a3c2-d51551c2dfaf', '1.91': '55d9467a-fc85-49a8-9bc6-8f6990e421e5', '2.40': '415112b3-69ff-4d53-8b10-cb4e3be68c9e', '3.10': 'ef67b600-3887-4225-b872-e354dfdf8454', '3.80': 'b16d3502-a9e4-4560-9775-852e9d07e70f', '4.50': '0c0bffc7-af77-4a56-a656-2a2610c991d6'}
Vérifions si toutes les tâches sont encore en cours d'exécution ou terminées.
completed_jobs_num = 0
running_jobs_num = 0
completed_jobs = {}
for i, info in enumerate(info_jobid.items()):
dis, job_id = info
submitted_job = catalog.get_job_by_id(job_id)
stat = submitted_job.status()
print(dis, submitted_job.job_id, stat)
if stat == "DONE":
completed_jobs_num += 1
completed_jobs[dis] = submitted_job
if (stat == "RUNNING") or (stat == "QUEUED"):
running_jobs_num += 1
print(
f"Completed {completed_jobs_num} job, Running or Queued {running_jobs_num} job"
)
1.51 de3b8818-c9db-4fa3-a3c2-d51551c2dfaf DONE
1.91 55d9467a-fc85-49a8-9bc6-8f6990e421e5 DONE
2.40 415112b3-69ff-4d53-8b10-cb4e3be68c9e DONE
3.10 ef67b600-3887-4225-b872-e354dfdf8454 DONE
3.80 b16d3502-a9e4-4560-9775-852e9d07e70f DONE
4.50 0c0bffc7-af77-4a56-a656-2a2610c991d6 DONE
Completed 6 job, Running or Queued 0 job
Une fois toutes les tâches terminées, récupérons tous les résultats de calcul.
hivqe_result = {}
if len(info_jobid) == completed_jobs_num:
print("All jobs are completed")
for i, job in enumerate(completed_jobs.items()):
dis, cal = job
print(dis, cal.result()["energy"])
hivqe_result[str(dis)] = cal.result()["energy"]
All jobs are completed
1.51 -407.8944801731773
1.91 -407.9800570932916
2.40 -407.9372992999806
3.10 -407.86278336000134
3.80 -407.83092972296157
4.50 -407.82971011225766
pprint.pprint(hivqe_result)
{'1.51': -407.8944801731773,
'1.91': -407.9800570932916,
'2.40': -407.9372992999806,
'3.10': -407.86278336000134,
'3.80': -407.83092972296157,
'4.50': -407.82971011225766}
Le temps d'exécution QPU total utilisé dans la tâche peut être suivi en te connectant à IBM Quantum Platform et en consultant les tâches soumises avec le tag qunova-chemistry-hivqe.
Étape 4 : Post-traitement et comparaison avec les méthodes classiques
Un calcul de référence classique (CASCI) peut être réalisé pour (10o,10e) afin de valider les résultats HiVQE.
str_geometries = {
"1.31": "S -1.250686 0.660708 -0.095168; Li -1.482812 0.453464 -1.369406; Li -0.911870 0.962810 1.762020",
"1.41": "S -1.244856 0.665971 -0.062773; Li -1.494574 0.442933 -1.434177; Li -0.905937 0.968078 1.794395",
"1.51": "S -1.239044 0.671232 -0.030374; Li -1.506327 0.432403 -1.498949; Li -0.899996 0.973348 1.826768",
"1.61": "S -1.233245 0.676492 0.002027; Li -1.518073 0.421873 -1.563722; Li -0.894049 0.978617 1.859141",
"1.71": "S -1.227453 0.681752 0.034429; Li -1.529816 0.411343 -1.628496; Li -0.888099 0.983887 1.891513",
"1.81": "S -1.221659 0.687012 0.066831; Li -1.541558 0.400813 -1.693270; Li -0.882150 0.989157 1.923885",
"1.91": "S -1.215858 0.692272 0.099232; Li -1.553305 0.390283 -1.758043; Li -0.876205 0.994426 1.956257",
"2.01": "S -1.209887 0.697544 0.131599; Li -1.565136 0.379748 -1.822800; Li -0.870344 0.999691 1.988646",
"2.11": "S -1.203945 0.702813 0.163973; Li -1.576953 0.369214 -1.887560; Li -0.864469 1.004956 2.021033",
"2.21": "S -1.198023 0.708081 0.196350; Li -1.588760 0.358680 -1.952322; Li -0.858584 1.010221 2.053417",
"2.30": "S -1.365426 0.717714 0.367060; Li -0.689401 0.458925 -1.828368; Li -1.500219 0.981173 2.255876",
"2.31": "S -1.192118 0.713348 0.228731; Li -1.600559 0.348146 -2.017085; Li -0.852690 1.015488 2.085800",
"2.40": "S -1.741432 0.680397 0.346702; Li -0.529307 0.488006 -1.729343; Li -1.284307 0.989409 2.177209",
"2.50": "S -1.885961 0.669986 0.365815; Li -0.461563 0.499084 -1.695846; Li -1.207523 0.988741 2.124599",
"2.60": "S -1.977163 0.665155 0.389784; Li -0.416654 0.504966 -1.683655; Li -1.161229 0.987690 2.088439",
"2.70": "S -2.063642 0.661518 0.418977; Li -0.367600 0.510505 -1.676408; Li -1.123804 0.985788 2.051998",
"2.80": "S -2.141072 0.659218 0.451663; Li -0.323153 0.515056 -1.673046; Li -1.090821 0.983538 2.015951",
"2.90": "S -2.212097 0.657968 0.487535; Li -0.281989 0.518909 -1.672407; Li -1.060960 0.980935 1.979440",
"3.00": "S -2.281477 0.657123 0.525155; Li -0.239607 0.523326 -1.668669; Li -1.033963 0.977363 1.938081",
"3.10": "S -2.347450 0.657089 0.566194; Li -0.199353 0.527517 -1.665148; Li -1.008243 0.973206 1.893522",
"3.20": "S -2.410882 0.657532 0.608912; Li -0.157788 0.532069 -1.659971; Li -0.986376 0.968211 1.845627",
"3.30": "S -2.470306 0.658818 0.654893; Li -0.118007 0.536237 -1.656311; Li -0.966733 0.962757 1.795986",
"3.40": "S -2.525776 0.660762 0.702910; Li -0.078312 0.540189 -1.654076; Li -0.950958 0.956861 1.745734",
"3.50": "S -2.576885 0.663376 0.752788; Li -0.039076 0.543706 -1.654536; Li -0.939085 0.950730 1.696316",
"3.60": "S -2.623930 0.666534 0.803853; Li 0.000274 0.546839 -1.657697; Li -0.931390 0.944439 1.648412",
"3.70": "S -2.667364 0.670217 0.856250; Li 0.039572 0.549616 -1.663265; Li -0.927254 0.937980 1.601583",
"3.80": "S -2.707255 0.674298 0.909161; Li 0.079218 0.552012 -1.671656; Li -0.927010 0.931502 1.557063",
"3.90": "S -2.744005 0.678718 0.962425; Li 0.119268 0.554073 -1.682595; Li -0.930310 0.925021 1.514738",
"4.00": "S -2.777891 0.683415 1.015798; Li 0.159751 0.555810 -1.696024; Li -0.936907 0.918587 1.474794",
"4.10": "S -2.809179 0.688333 1.069057; Li 0.200678 0.557234 -1.711873; Li -0.946546 0.912245 1.437385",
"4.20": "S -2.838194 0.693443 1.122205; Li 0.242066 0.558401 -1.729770; Li -0.958918 0.905968 1.402134",
"4.30": "S -2.864984 0.698619 1.174415; Li 0.283858 0.559186 -1.750539; Li -0.973920 0.900007 1.370693",
"4.40": "S -2.889984 0.703887 1.226140; Li 0.326068 0.559728 -1.773231; Li -0.991131 0.894196 1.341660",
"4.50": "S -2.913363 0.709175 1.276987; Li 0.368656 0.559989 -1.798088; Li -1.010340 0.888647 1.315670",
}
rhf_result = {}
casci_result = {}
cas_list = molecule_options["active_orbitals"]
distance_ref = []
for dis, geom in str_geometries.items():
distance_ref.append(dis)
mole = gto.M(atom=geom, basis=molecule_options["basis"])
mole.verbose = 0
# RHF energy
mf = scf.RHF(mole).run()
mo_occ = mf.mo_occ
num_elecs_as = int(sum([mo_occ[idx] for idx in cas_list]))
rhf_result[str(dis)] = mf.e_tot
# CASCI energy
casci_solver = mcscf.CASCI(mf, len(cas_list), num_elecs_as)
orbs = mcscf.addons.sort_mo(casci_solver, mf.mo_coeff, cas_list, base=0)
casci_solver.kernel(orbs)
casci_result[str(dis)] = casci_solver.e_tot
print(
f"d={dis:4.3} RHF Energy: {mf.e_tot:14.10}, CASCI Energy: {casci_solver.e_tot:14.10}"
)
d=1.3 RHF Energy: -407.7137006, CASCI Energy: -407.7193917
d=1.4 RHF Energy: -407.8183196, CASCI Energy: -407.8245211
d=1.5 RHF Energy: -407.8878013, CASCI Energy: -407.8944802
d=1.6 RHF Energy: -407.9315356, CASCI Energy: -407.9385663
d=1.7 RHF Energy: -407.9569034, CASCI Energy: -407.9641258
d=1.8 RHF Energy: -407.9693681, CASCI Energy: -407.9766313
d=1.9 RHF Energy: -407.9728592, CASCI Energy: -407.9800572
d=2.0 RHF Energy: -407.9701684, CASCI Energy: -407.9772549
d=2.1 RHF Energy: -407.9632701, CASCI Energy: -407.9702381
d=2.2 RHF Energy: -407.9535584, CASCI Energy: -407.9604007
d=2.3 RHF Energy: -407.9420173, CASCI Energy: -407.9487043
d=2.3 RHF Energy: -407.9420156, CASCI Energy: -407.9487024
d=2.4 RHF Energy: -407.9297216, CASCI Energy: -407.9372993
d=2.5 RHF Energy: -407.9172, CASCI Energy: -407.9261859
d=2.6 RHF Energy: -407.9061139, CASCI Energy: -407.915961
d=2.7 RHF Energy: -407.8937118, CASCI Energy: -407.904259
d=2.8 RHF Energy: -407.8816389, CASCI Energy: -407.8928292
d=2.9 RHF Energy: -407.8700448, CASCI Energy: -407.8819574
d=3.0 RHF Energy: -407.859054, CASCI Energy: -407.8719092
d=3.1 RHF Energy: -407.8487619, CASCI Energy: -407.8628304
d=3.2 RHF Energy: -407.8392304, CASCI Energy: -407.8548482
d=3.3 RHF Energy: -407.8304842, CASCI Energy: -407.8480217
d=3.4 RHF Energy: -407.8225124, CASCI Energy: -407.8423743
d=3.5 RHF Energy: -407.8152758, CASCI Energy: -407.8378892
d=3.6 RHF Energy: -407.8087161, CASCI Energy: -407.8345331
d=3.7 RHF Energy: -407.802764, CASCI Energy: -407.8322563
d=3.8 RHF Energy: -407.7973458, CASCI Energy: -407.83093
d=3.9 RHF Energy: -407.7923883, CASCI Energy: -407.8303555
d=4.0 RHF Energy: -407.7878216, CASCI Energy: -407.83025
d=4.1 RHF Energy: -407.783582, CASCI Energy: -407.8303243
d=4.2 RHF Energy: -407.7796124, CASCI Energy: -407.8303791
d=4.3 RHF Energy: -407.7758633, CASCI Energy: -407.8302885
d=4.4 RHF Energy: -407.7722923, CASCI Energy: -407.8300614
d=4.5 RHF Energy: -407.7688641, CASCI Energy: -407.829711
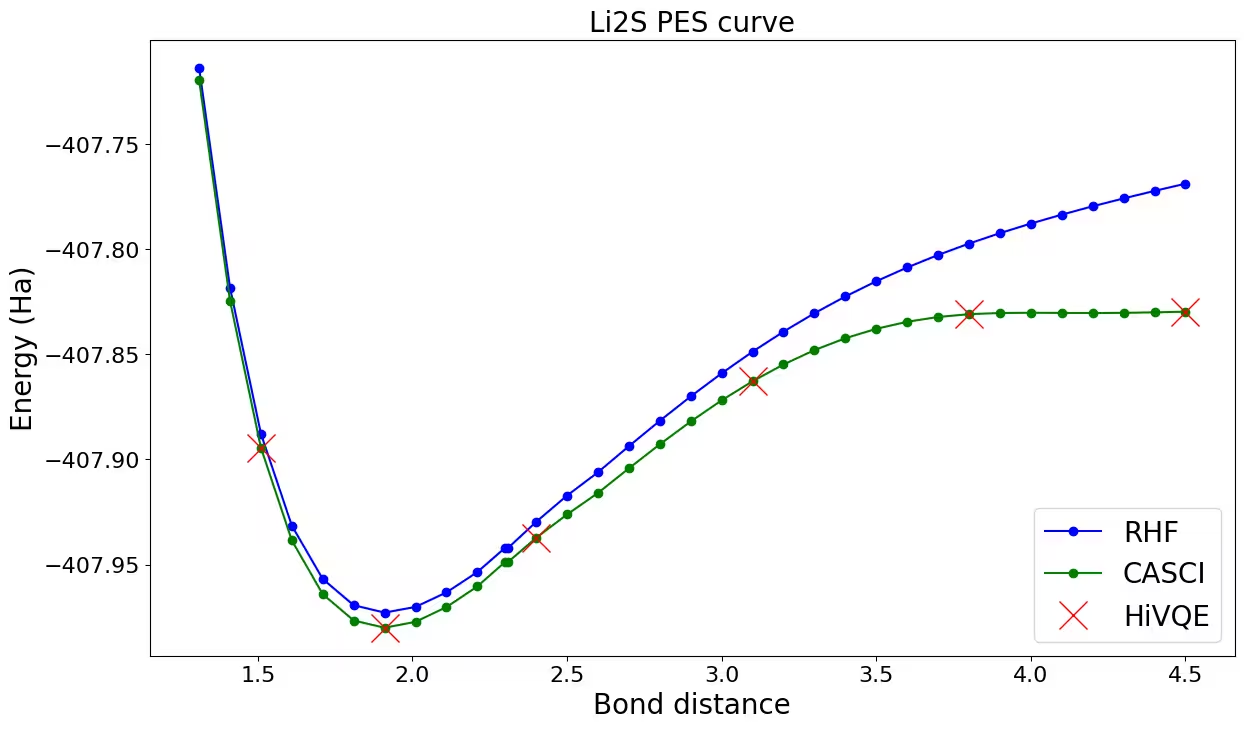
Traçage de la courbe de dissociation pour Li_2S
Traçons et comparons les résultats HiVQE avec HF et CASCI. Vous pouvez observer que tous les calculs HiVQE correspondent bien au résultat de référence classique (CASCI).
fig, ax = plt.subplots(1, 1)
hf_energy = [v for key, v in rhf_result.items()]
casci_energy = [v for key, v in casci_result.items()]
hivqe_energy = [v for key, v in hivqe_result.items()]
distance_ref = [float(key) for key, v in rhf_result.items()]
distance = [float(key) for key, v in hivqe_result.items()]
ax.plot(distance_ref, hf_energy, "-o", label="RHF", c="blue")
ax.plot(distance_ref, casci_energy, "-o", label="CASCI", c="green")
ax.plot(distance, hivqe_energy, "x", label="HiVQE", c="red", markersize=20)
ax.legend(fontsize=20)
ax.tick_params("both", labelsize=16)
ax.set_xlabel("Bond distance (angstrom)", size=20)
ax.set_ylabel("Energy (Ha)", size=20)
ax.set_title("Li2S PES curve", size=20)
fig.set_size_inches(14, 8)
Partie 2 : FeP-NO (44Q)
Note : pour exécuter la fonction sur le système FeP-NO avec les paramètres indiqués dans cet exemple, tu dois disposer d'une licence permettant l'utilisation de la fonction avec au moins 44 qubits. Envoie un e-mail à qiskit.support@qunovacomputing.com pour obtenir des informations sur l'obtention d'une licence.
Étape 1 : Mapper les entrées classiques sur un problème quantique
Définissez les options pour les calculs HiVQE
molecule_options = {
"basis": "631g*",
"active_orbitals": list(range(90, 112, 1)),
"frozen_orbitals": list(range(0, 90, 1)),
"charge": -1,
}
hivqe_options = {
"shots": 2000,
"max_iter": 40,
"ansatz": "epa",
"ansatz_entanglement": "linear",
"ansatz_reps": 2,
"amplitude_screening_tolerance": 1e-6,
}
Définissez les géométries de FeP-NO au format dictionnaire pour différentes distances de liaison Fe-N afin de calculer la courbe PES.
geometry_1_75 = """
Fe 9.910596 31.534095 1.798088
N 10.557481 31.888419 -0.055204
N 11.823496 31.255002 2.384659
N 9.292831 30.783362 3.568730
N 8.036805 31.418327 1.124265
C 9.784765 32.177349 -1.158798
C 10.612656 32.501029 -2.296868
C 11.903375 32.404043 -1.876832
C 11.859093 32.028943 -0.483750
C 12.965737 31.464698 1.641427
C 14.146517 31.236323 2.440231
C 13.713061 30.885870 3.681911
C 12.268752 30.896411 3.634891
C 10.067717 30.486167 4.664747
C 9.246224 30.053411 5.772052
C 7.957075 30.082846 5.336488
C 7.995710 30.538421 3.967046
C 6.900258 31.104497 1.836595
C 5.722470 31.251707 1.015333
C 6.148430 31.668586 -0.207993
C 7.587039 31.767438 -0.130483
C 8.399453 32.134197 -1.192329
H 7.912872 32.388031 -2.131079
C 12.984883 31.836053 0.306093
H 13.955948 31.977044 -0.162626
C 11.453768 30.560663 4.708020
H 11.940677 30.298823 5.644352
C 6.877071 30.697580 3.164102
H 5.907240 30.476797 3.603674
H 12.813946 32.569160 -2.441577
H 10.236332 32.758110 -3.280309
H 15.164312 31.335191 2.080201
H 14.299625 30.629109 4.556760
H 9.626524 29.758225 6.743433
H 7.053076 29.823583 5.875809
H 4.709768 31.058315 1.350561
H 5.561898 31.886355 -1.093106
N 9.832739 33.209042 2.298783
O 9.346337 34.075996 1.606023
"""
geometry_2_00 = """
Fe 9.917990 31.445558 1.778346
N 10.556809 31.866188 -0.055498
N 11.814089 31.227003 2.372666
N 9.297875 30.758246 3.550104
N 8.043584 31.397768 1.120485
C 9.784831 32.164652 -1.160219
C 10.611624 32.501801 -2.293514
C 11.902858 32.406547 -1.875160
C 11.859552 32.017818 -0.486307
C 12.960503 31.454432 1.636717
C 14.140770 31.242960 2.439615
C 13.708543 30.884151 3.678983
C 12.266351 30.874173 3.627468
C 10.070264 30.465070 4.655102
C 9.247247 30.053101 5.766681
C 7.958085 30.091201 5.332866
C 7.998432 30.529979 3.958727
C 6.901428 31.093932 1.833807
C 5.723289 31.255057 1.016540
C 6.151314 31.670649 -0.206350
C 7.589736 31.755538 -0.133074
C 8.400230 32.124963 -1.194447
H 7.913264 32.386655 -2.130914
C 12.983905 31.827747 0.302415
H 13.955696 31.979687 -0.161365
C 11.454251 30.533644 4.698234
H 11.941002 30.276716 5.636156
C 6.877444 30.689985 3.159940
H 5.907605 30.480118 3.604825
H 12.813105 32.581608 -2.437367
H 10.233725 32.768337 -3.273979
H 15.157796 31.357524 2.082132
H 14.295001 30.638320 4.557047
H 9.626721 29.768762 6.741623
H 7.051752 29.847502 5.875478
H 4.709710 31.071712 1.354640
H 5.565103 31.898376 -1.089333
N 9.840508 33.353531 2.373019
O 9.344561 34.158205 1.637232
"""
geometry_5_00 = """
Fe 9.918629 31.289202 1.717339
N 10.542914 31.832173 -0.080685
N 11.795572 31.199413 2.341831
N 9.294593 30.741247 3.513929
N 8.042689 31.359481 1.087282
C 9.775254 32.111817 -1.200449
C 10.600219 32.479101 -2.319680
C 11.891090 32.425876 -1.887580
C 11.847694 32.024341 -0.507342
C 12.945734 31.464689 1.611366
C 14.116395 31.289997 2.423572
C 13.685777 30.915122 3.663719
C 12.252381 30.861042 3.608186
C 10.062170 30.463021 4.634102
C 9.236749 30.104333 5.755782
C 7.945687 30.161198 5.324720
C 7.989641 30.552269 3.941498
C 6.892881 31.087489 1.815829
C 5.722676 31.253502 1.001149
C 6.153153 31.631057 -0.238233
C 7.586010 31.695401 -0.179773
C 8.390724 32.047572 -1.247553
H 7.903308 32.291586 -2.187969
C 12.973334 31.849872 0.283741
H 13.944682 32.031190 -0.169145
C 11.447158 30.518591 4.678739
H 11.934423 30.277429 5.619969
C 6.864795 30.711643 3.146118
H 5.893357 30.532078 3.599511
H 12.800139 32.636412 -2.439296
H 10.224017 32.743662 -3.301293
H 15.131785 31.441247 2.076257
H 14.273933 30.694315 4.546802
H 9.612512 29.848040 6.739754
H 7.036117 29.960530 5.879248
H 4.707408 31.099933 1.347803
H 5.564992 31.851940 -1.121294
N 9.666041 36.091609 3.085945
O 9.598728 37.226756 3.411299
"""
str_geometries = {
"1.75": geometry_1_75,
"2.00": geometry_2_00,
"5.00": geometry_5_00,
}
hivqe_result = {}
{'5.0': '\nFe 9.918629 31.289202 1.717339\nN 10.542914 31.832173 -0.080685\nN 11.795572 31.199413 2.341831\nN 9.294593 30.741247 3.513929\nN 8.042689 31.359481 1.087282\nC 9.775254 32.111817 -1.200449\nC 10.600219 32.479101 -2.319680\nC 11.891090 32.425876 -1.887580\nC 11.847694 32.024341 -0.507342\nC 12.945734 31.464689 1.611366\nC 14.116395 31.289997 2.423572\nC 13.685777 30.915122 3.663719\nC 12.252381 30.861042 3.608186\nC 10.062170 30.463021 4.634102\nC 9.236749 30.104333 5.755782\nC 7.945687 30.161198 5.324720\nC 7.989641 30.552269 3.941498\nC 6.892881 31.087489 1.815829\nC 5.722676 31.253502 1.001149\nC 6.153153 31.631057 -0.238233\nC 7.586010 31.695401 -0.179773\nC 8.390724 32.047572 -1.247553\nH 7.903308 32.291586 -2.187969\nC 12.973334 31.849872 0.283741\nH 13.944682 32.031190 -0.169145\nC 11.447158 30.518591 4.678739\nH 11.934423 30.277429 5.619969\nC 6.864795 30.711643 3.146118\nH 5.893357 30.532078 3.599511\nH 12.800139 32.636412 -2.439296\nH 10.224017 32.743662 -3.301293\nH 15.131785 31.441247 2.076257\nH 14.273933 30.694315 4.546802\nH 9.612512 29.848040 6.739754\nH 7.036117 29.960530 5.879248\nH 4.707408 31.099933 1.347803\nH 5.564992 31.851940 -1.121294\nN 9.666041 36.091609 3.085945\nO 9.598728 37.226756 3.411299\n'}
geometry_1_75 = """
Fe 9.910596 31.534095 1.798088
N 10.557481 31.888419 -0.055204
N 11.823496 31.255002 2.384659
N 9.292831 30.783362 3.568730
N 8.036805 31.418327 1.124265
C 9.784765 32.177349 -1.158798
C 10.612656 32.501029 -2.296868
C 11.903375 32.404043 -1.876832
C 11.859093 32.028943 -0.483750
C 12.965737 31.464698 1.641427
C 14.146517 31.236323 2.440231
C 13.713061 30.885870 3.681911
C 12.268752 30.896411 3.634891
C 10.067717 30.486167 4.664747
C 9.246224 30.053411 5.772052
C 7.957075 30.082846 5.336488
C 7.995710 30.538421 3.967046
C 6.900258 31.104497 1.836595
C 5.722470 31.251707 1.015333
C 6.148430 31.668586 -0.207993
C 7.587039 31.767438 -0.130483
C 8.399453 32.134197 -1.192329
H 7.912872 32.388031 -2.131079
C 12.984883 31.836053 0.306093
H 13.955948 31.977044 -0.162626
C 11.453768 30.560663 4.708020
H 11.940677 30.298823 5.644352
C 6.877071 30.697580 3.164102
H 5.907240 30.476797 3.603674
H 12.813946 32.569160 -2.441577
H 10.236332 32.758110 -3.280309
H 15.164312 31.335191 2.080201
H 14.299625 30.629109 4.556760
H 9.626524 29.758225 6.743433
H 7.053076 29.823583 5.875809
H 4.709768 31.058315 1.350561
H 5.561898 31.886355 -1.093106
N 9.832739 33.209042 2.298783
O 9.346337 34.075996 1.606023
"""
geometry_2_00 = """
Fe 9.917990 31.445558 1.778346
N 10.556809 31.866188 -0.055498
N 11.814089 31.227003 2.372666
N 9.297875 30.758246 3.550104
N 8.043584 31.397768 1.120485
C 9.784831 32.164652 -1.160219
C 10.611624 32.501801 -2.293514
C 11.902858 32.406547 -1.875160
C 11.859552 32.017818 -0.486307
C 12.960503 31.454432 1.636717
C 14.140770 31.242960 2.439615
C 13.708543 30.884151 3.678983
C 12.266351 30.874173 3.627468
C 10.070264 30.465070 4.655102
C 9.247247 30.053101 5.766681
C 7.958085 30.091201 5.332866
C 7.998432 30.529979 3.958727
C 6.901428 31.093932 1.833807
C 5.723289 31.255057 1.016540
C 6.151314 31.670649 -0.206350
C 7.589736 31.755538 -0.133074
C 8.400230 32.124963 -1.194447
H 7.913264 32.386655 -2.130914
C 12.983905 31.827747 0.302415
H 13.955696 31.979687 -0.161365
C 11.454251 30.533644 4.698234
H 11.941002 30.276716 5.636156
C 6.877444 30.689985 3.159940
H 5.907605 30.480118 3.604825
H 12.813105 32.581608 -2.437367
H 10.233725 32.768337 -3.273979
H 15.157796 31.357524 2.082132
H 14.295001 30.638320 4.557047
H 9.626721 29.768762 6.741623
H 7.051752 29.847502 5.875478
H 4.709710 31.071712 1.354640
H 5.565103 31.898376 -1.089333
N 9.840508 33.353531 2.373019
O 9.344561 34.158205 1.637232
"""
geometry_5_00 = """
Fe 9.918629 31.289202 1.717339
N 10.542914 31.832173 -0.080685
N 11.795572 31.199413 2.341831
N 9.294593 30.741247 3.513929
N 8.042689 31.359481 1.087282
C 9.775254 32.111817 -1.200449
C 10.600219 32.479101 -2.319680
C 11.891090 32.425876 -1.887580
C 11.847694 32.024341 -0.507342
C 12.945734 31.464689 1.611366
C 14.116395 31.289997 2.423572
C 13.685777 30.915122 3.663719
C 12.252381 30.861042 3.608186
C 10.062170 30.463021 4.634102
C 9.236749 30.104333 5.755782
C 7.945687 30.161198 5.324720
C 7.989641 30.552269 3.941498
C 6.892881 31.087489 1.815829
C 5.722676 31.253502 1.001149
C 6.153153 31.631057 -0.238233
C 7.586010 31.695401 -0.179773
C 8.390724 32.047572 -1.247553
H 7.903308 32.291586 -2.187969
C 12.973334 31.849872 0.283741
H 13.944682 32.031190 -0.169145
C 11.447158 30.518591 4.678739
H 11.934423 30.277429 5.619969
C 6.864795 30.711643 3.146118
H 5.893357 30.532078 3.599511
H 12.800139 32.636412 -2.439296
H 10.224017 32.743662 -3.301293
H 15.131785 31.441247 2.076257
H 14.273933 30.694315 4.546802
H 9.612512 29.848040 6.739754
H 7.036117 29.960530 5.879248
H 4.707408 31.099933 1.347803
H 5.564992 31.851940 -1.121294
N 9.666041 36.091609 3.085945
O 9.598728 37.226756 3.411299
"""
str_geometries = {
"1.75": geometry_1_75,
"2.00": geometry_2_00,
"5.00": geometry_5_00,
}
hivqe_result = {}
{'5.0': '\nFe 9.918629 31.289202 1.717339\nN 10.542914 31.832173 -0.080685\nN 11.795572 31.199413 2.341831\nN 9.294593 30.741247 3.513929\nN 8.042689 31.359481 1.087282\nC 9.775254 32.111817 -1.200449\nC 10.600219 32.479101 -2.319680\nC 11.891090 32.425876 -1.887580\nC 11.847694 32.024341 -0.507342\nC 12.945734 31.464689 1.611366\nC 14.116395 31.289997 2.423572\nC 13.685777 30.915122 3.663719\nC 12.252381 30.861042 3.608186\nC 10.062170 30.463021 4.634102\nC 9.236749 30.104333 5.755782\nC 7.945687 30.161198 5.324720\nC 7.989641 30.552269 3.941498\nC 6.892881 31.087489 1.815829\nC 5.722676 31.253502 1.001149\nC 6.153153 31.631057 -0.238233\nC 7.586010 31.695401 -0.179773\nC 8.390724 32.047572 -1.247553\nH 7.903308 32.291586 -2.187969\nC 12.973334 31.849872 0.283741\nH 13.944682 32.031190 -0.169145\nC 11.447158 30.518591 4.678739\nH 11.934423 30.277429 5.619969\nC 6.864795 30.711643 3.146118\nH 5.893357 30.532078 3.599511\nH 12.800139 32.636412 -2.439296\nH 10.224017 32.743662 -3.301293\nH 15.131785 31.441247 2.076257\nH 14.273933 30.694315 4.546802\nH 9.612512 29.848040 6.739754\nH 7.036117 29.960530 5.879248\nH 4.707408 31.099933 1.347803\nH 5.564992 31.851940 -1.121294\nN 9.666041 36.091609 3.085945\nO 9.598728 37.226756 3.411299\n'}
Étapes 2 et 3 : Optimiser le problème pour l'exécution sur matériel quantique et exécuter avec la fonction HiVQE Chemistry
Sur la base de la configuration de HiVQE et des géométries, obtenez les résultats séquentiellement.
Soumettre le calcul pour d(Fe-N) = 1.75 .
hivqe_run_1_75 = hivqe.run(
geometry=str_geometries["1.75"],
backend_name="",
max_states=400000000,
max_expansion_states=100,
molecule_options=molecule_options,
hivqe_options=hivqe_options,
)
info_jobid_1_75 = hivqe_run_1_75.job_id
Suivez la tâche et récupérez le résultat pour le calcul d(Fe-N) = 1.75 .
submitted_job_1_75 = catalog.get_job_by_id(info_jobid_1_75)
stat = submitted_job_1_75.status()
print(submitted_job_1_75.job_id, stat)
if stat == "DONE":
hivqe_run_1_75_energy = submitted_job_1_75.result()["energy"]
print(f"Completed HiVQE calculation, Energy {hivqe_run_1_75_energy}")
hivqe_result["1.75"] = hivqe_run_1_75_energy
Soumettre le calcul pour d(Fe-N) = 2.00 .
hivqe_run_2_00 = hivqe.run(
geometry=str_geometries["2.00"],
backend_name="",
max_states=400000000,
max_expansion_states=100,
molecule_options=molecule_options,
hivqe_options=hivqe_options,
)
info_jobid_2_00 = hivqe_run_2_00.job_id
Suivez la tâche et récupérez le résultat pour le calcul d(Fe-N) = 2.00 .
submitted_job_2_00 = catalog.get_job_by_id(info_jobid_2_00)
stat = submitted_job_2_00.status()
print(submitted_job_2_00.job_id, stat)
if stat == "DONE":
hivqe_run_2_00_energy = submitted_job_2_00.result()["energy"]
print(f"Completed HiVQE calculation, Energy {hivqe_run_2_00_energy}")
hivqe_result["2.00"] = hivqe_run_2_00_energy
Soumettre le calcul pour d(Fe-N) = 5.00 .
hivqe_run_5_00 = hivqe.run(
geometry=str_geometries["5.00"],
backend_name="",
max_states=400000000,
max_expansion_states=100,
molecule_options=molecule_options,
hivqe_options=hivqe_options,
)
info_jobid_5_00 = hivqe_run_5_00.job_id
Suivez la tâche et récupérez le résultat pour le calcul d(Fe-N) = 5.00 .
submitted_job_5_00 = catalog.get_job_by_id(info_jobid_5_00)
stat = submitted_job_5_00.status()
print(submitted_job_5_00.job_id, stat)
if stat == "DONE":
hivqe_run_5_00_energy = submitted_job_5_00.result()["energy"]
print(f"Completed HiVQE calculation, Energy {hivqe_run_5_00_energy}")
hivqe_result["5.00"] = hivqe_run_5_00_energy
hivqe_result = {
"1.75": -2373.681781,
"2.00": -2373.694128,
"5.00": -2373.637807,
}
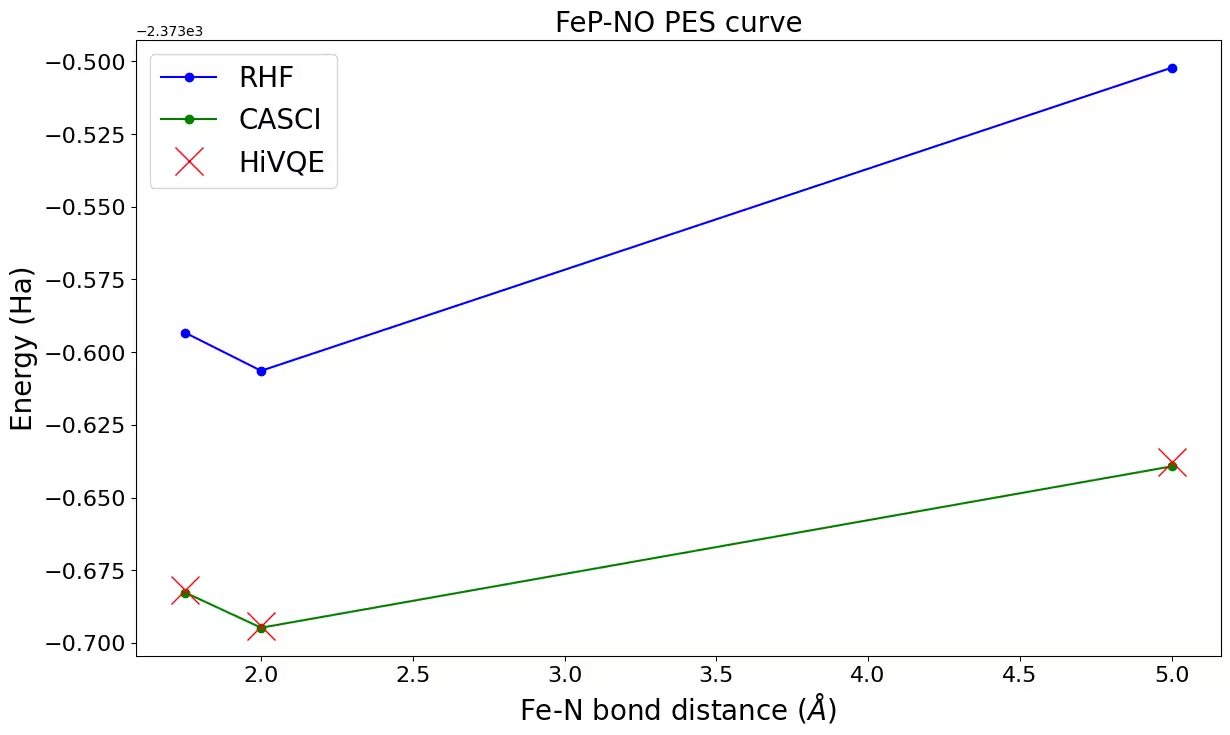
Étape 4 : Post-traitement et comparaison avec les méthodes classiques
Les résultats du calcul de référence classique (CASCI-DMRG, maxM=800) sont fournis pour (22o,22e) afin de valider les résultats HiVQE.
rhf_result = {
"1.75": -2373.59331683504,
"2.00": -2373.60640773065,
"5.00": -2373.50214278007,
}
casci_result = {"1.75": -2373.6827, "2.00": -2373.6948, "5.00": -2373.6393}
fig, ax = plt.subplots(1, 1)
hf_energy = [v for key, v in rhf_result.items()]
casci_energy = [v for key, v in casci_result.items()]
hivqe_energy = [v for key, v in hivqe_result.items()]
distance_ref = [float(key) for key, v in rhf_result.items()]
distance = [float(key) for key, v in hivqe_result.items()]
ax.plot(distance_ref, hf_energy, "-o", label="RHF", c="blue")
ax.plot(distance_ref, casci_energy, "-o", label="CASCI", c="green")
ax.plot(distance, hivqe_energy, "x", label="HiVQE", c="red", markersize=20)
ax.legend(fontsize=20)
ax.tick_params("both", labelsize=16)
ax.set_xlabel("Fe-N bond distance ($\AA$)", size=20)
ax.set_ylabel("Energy (Ha)", size=20)
ax.set_title("FeP-NO PES curve", size=20)
fig.set_size_inches(14, 8)
Enquête sur le tutoriel
Réponds à cette courte enquête pour donner ton avis sur ce tutoriel. Tes retours nous aideront à améliorer nos contenus et l'expérience utilisateur.
Note: This survey is provided by IBM Quantum and relates to the original English content. To give feedback on doQumentation's website, translations, or code execution, please open a GitHub issue.